

const { OpenAI } = require('openai');
const api = new OpenAI({ apiKey: '', baseURL: 'https://api.ai.cc/v1' });
const main = async () => {
const prompt = `
All of the states in the USA:
- Alabama, Mongomery;
- Arkansas, Little Rock;
`;
const response = await api.completions.create({
prompt,
model: 'togethercomputer/evo-1-131k-base',
});
const text = response.choices[0].text;
console.log('Completion:', text);
};
main();
from openai import OpenAI
client = OpenAI(
api_key="",
base_url="https://api.ai.cc/v1",
)
def main():
response = client.completions.create(
model="togethercomputer/evo-1-131k-base",
prompt="""
All of the states in the USA:
- Alabama, Mongomery;
- Arkansas, Little Rock;
""",
)
completion = response.choices[0].text
print(f"Completion: {completion}")
main()

Detalles del producto
✨ Evo-1 Base (131K): Un análisis a fondo
Evo-1 Base (131K) representa un avance significativo en el modelado de IA, diseñado específicamente para el procesamiento sofisticado de texto y secuencias genómicas. Desarrollado por Together Computer, este modelo aprovecha una arquitectura de vanguardia para ofrecer un rendimiento sin precedentes en la comprensión y generación de datos biológicos complejos, además de realizar tareas lingüísticas tradicionales.
Información básica
- ✨ Nombre del modelo: Evo-1 Base (131K)
- 🚀 Desarrollador/Creador: Computadora conjunta
- 📅 Fecha de lanzamiento: 25 de febrero de 2024
- ⚙️ Versión: 1.1
- 💡 Tipo de modelo: Modelo de IA de conversión de texto a texto
Características y capacidades clave
Evo-1 Base (131K) se basa en una arquitectura única que le permite manejar tareas complejas con gran cantidad de datos de entrada, lo que la distingue en el panorama de la IA.
- ✅ 7 mil millones de parámetros: Proporciona amplias capacidades de modelado para diversas aplicaciones.
- ✅ Arquitectura de Hiena Rayada: Mejora la eficiencia del procesamiento de secuencias, especialmente en contextos largos.
- ✅ Modelado a nivel de nucleótido único: Capaz de realizar análisis precisos de secuencias genómicas.
- ✅ Entrenado en OpenGenome: Se beneficia de un conjunto de datos exhaustivo de aproximadamente 300 mil millones de tokens.
- ✅ Soporte para contextos extensos: Procesa entradas de hasta 131.000 tokens, ideal para tareas complejas.
Uso previsto
Evo-1 está diseñado principalmente para aplicaciones en genómica, bioinformática y otros campos que requieren modelado de secuencias de alta resolución. Su versatilidad también se extiende a tareas de lenguaje general.
- 🧬 Análisis de datos genómicos: Generación y análisis avanzados de secuencias de ADN.
- ✍️ Automatización de contenido: Automatización de la generación de contenido para diversas necesidades.
- 💬 Desarrollo de chatbots: Desarrollo de chatbots sofisticados y aplicaciones de comprensión del lenguaje.
- 🌐 Tareas de idiomas: Tareas eficientes de traducción y resumen de idiomas.
Soporte lingüístico
El modelo principalmente admite Inglés, junto con varios formatos de secuencias biológicas para aplicaciones especializadas.
Especificaciones técnicas
Arquitectura
El Evo-1 utiliza el Arquitectura de Hiena RayadaSe trata de un diseño híbrido que combina atención multi-cabeza y convoluciones con compuerta. Este enfoque innovador permite el procesamiento eficiente de secuencias excepcionalmente largas, superando a los modelos transformadores tradicionales en contextos específicos.
Datos de entrenamiento
El modelo fue entrenado rigurosamente en el conjunto de datos OpenGenome, una extensa colección de secuencias de genomas completos procariotas. Comprende aproximadamente 300 mil millones de tokensEste conjunto de datos proporciona una base sólida para el aprendizaje de secuencias biológicas complejas. Esto contrasta con muchos modelos genómicos que suelen entrenarse con conjuntos de datos más pequeños y especializados, lo que puede limitar su capacidad de generalización.
umbral de conocimiento
La base de conocimientos de Evo-1 está actualizada a partir de Febrero de 2024.
Diversidad y prejuicios
La exhaustividad de los datos de entrenamiento, que abarcan una amplia gama de genomas procariotas, contribuye significativamente a reducir el sesgo y a mejorar la capacidad del modelo para generalizar en diversos contextos biológicos.
Métricas de rendimiento
Evo-1 Base (131K) ha demostrado un rendimiento excepcional en diversas pruebas comparativas y tareas genómicas especializadas:
- 📈 Precisión: 89,5% en las pruebas de referencia comunes para la clasificación de texto.
- 📊 Perplejidad: 8.3 en el conjunto de datos Wikitext-103.
- ⭐ Puntuación F1: 92,7 en tareas de resumen.
- ⚡ Velocidad: Procesa aproximadamente 12 ms por token, lo que permite aplicaciones en tiempo real.
- 🛡️ Robustez: Gestiona de forma eficiente las consultas ambiguas y la generación de código, demostrando una flexibilidad notable.
Capacidades genómicas de vanguardia
- 🔬 Predicción de funciones sin necesidad de pruebas adicionales: Compite con los modelos especializados específicos de cada dominio y, a menudo, los supera en la predicción de los efectos de las mutaciones sobre la aptitud biológica.
- 🧪 Generación de múltiples elementos: Destaca por generar estructuras moleculares complejas, una capacidad novedosa para la biología sintética.
- 🧬 Predicción de la esencialidad de los genes: Predice con precisión la esencialidad de los genes a nivel de nucleótido, algo crucial para comprender las funciones genéticas.
Comparación con otros modelos

El modelo Evo-1 Base (131K) se distingue como una herramienta altamente especializada para análisis genómico evolutivoSi bien modelos como AlphaFold y RoseTTAFold son líderes en la predicción de la estructura de proteínas, Evo-1 Base está dirigido específicamente a investigadores centrados en datos genómicos a gran escala, en particular para explorar patrones evolutivos y detectar mutaciones en diferentes especies.
Su eficiencia con vastos conjuntos de datos genómicos lo hace indispensable para la biología evolutiva, la genómica comparativa y la detección de mutaciones. A diferencia de los modelos centrados en proteínas como ESM y ProtBert, la arquitectura de Evo-1 Base está finamente ajustada para conocimientos genómicosposicionándola como una opción poderosa para avanzar en la investigación en genómica y comprender las fuerzas evolutivas de la vida.
Uso e integración
Ejemplos de código
El modelo Evo-1 está disponible en el Plataforma API de IA/ML bajo el identificador togethercomputer/evo-1-131k-base.
Documentación de la API
Para obtener directrices de integración completas, consulte la información detallada. Documentación de la API Está disponible en el sitio web de la API de IA/ML.
Directrices éticas y licencias
Directrices éticas
El desarrollo del Evo-1 se adhiere estrictamente a Estándares éticos de IA y bioinformática, haciendo hincapié en el uso responsable y la minimización activa de los posibles sesgos en el análisis de datos genómicos.
Licencias
El modelo se lanza bajo el Licencia Apache 2.0, otorgando amplios derechos tanto para uso comercial como no comercial.
❓ Preguntas frecuentes (FAQ)
P: ¿Qué hace que Evo-1 Base (131K) sea único para el análisis genómico?
A: Evo-1 destaca por su arquitectura StripedHyena, que permite el procesamiento de contexto extenso (hasta 131 000 tokens) y el entrenamiento con el vasto conjunto de datos OpenGenome. Esto posibilita una resolución sin precedentes en el modelado de secuencias genómicas, incluyendo el análisis a nivel de nucleótido único y tareas avanzadas como la generación de múltiples elementos.
P: ¿Se puede utilizar Evo-1 Base para tareas lingüísticas generales o solo para genómica?
A: Si bien Evo-1 Base está altamente especializado en genómica y bioinformática, es un modelo de IA versátil para la conversión de texto a texto. Puede manejar eficazmente tareas lingüísticas generales como la generación de contenido, el resumen, la traducción y el desarrollo de chatbots, principalmente en inglés.
P: ¿Cuál es el significado de la arquitectura de la Hiena Rayada?
A: La arquitectura StripedHyena es un diseño híbrido que combina atención multi-cabeza y convoluciones con compuerta. Esta innovación permite que Evo-1 procese secuencias largas de manera más eficiente que los modelos Transformer tradicionales, lo cual es crucial para tareas complejas que requieren gran cantidad de datos de entrada, especialmente en genómica.
P: ¿Cómo se compara Evo-1 con otros modelos de IA destacados en biología?
A: Evo-1 está especialmente diseñado para el análisis genómico evolutivo y la detección de mutaciones, lo que lo diferencia de modelos como AlphaFold y RoseTTAFold (centrados en la predicción de la estructura de proteínas) o ESM y ProtBert (optimizados para secuencias de proteínas). La fortaleza de Evo-1 reside en la interpretación de datos genómicos a gran escala y la comprensión de patrones evolutivos.
P: ¿Bajo qué licencia se publica Evo-1 Base (131K)?
A: Evo-1 Base (131K) se publica bajo la licencia Apache 2.0, que permite tanto el uso comercial como el no comercial, ofreciendo una gran flexibilidad para desarrolladores e investigadores.
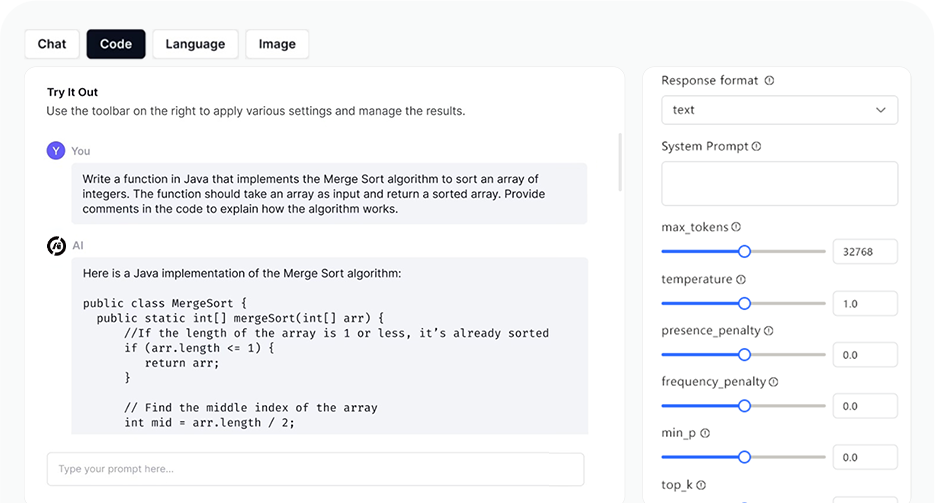
Campo de juegos de IA


 Acceso
Acceso